Um novo genótipo de H5N1 avançou rapidamente pelas rotas migratórias
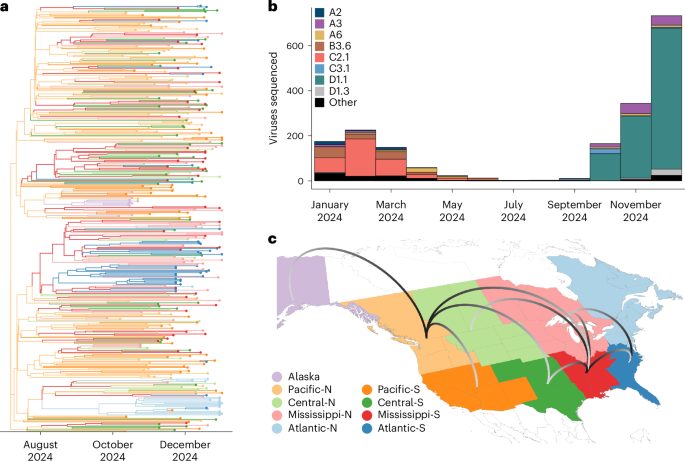
Um estudo publicado on-line na Nature Medicine em 15 de abril de 2026 informa que um genótipo recém-classificado de influenza aviária altamente patogênica, D1.1, se expandiu rapidamente em aves silvestres da América do Norte durante a temporada migratória de 2024. O artigo descreve o vírus como um reassortante, detectado pela primeira vez em setembro de 2024 e depois acompanhado por meio de programas de vigilância ativa e passiva no Canadá e nos Estados Unidos.
A principal conclusão não é apenas que o H5N1 permaneceu presente em populações de aves silvestres, mas que um genótipo distinto parece ter se espalhado com rapidez suficiente para deslocar linhagens A(H5) anteriores em várias rotas migratórias. Isso importa porque as rotas migratórias são os canais pelos quais a influenza aviária pode se mover por longas distâncias, cruzar jurisdições e semear novos surtos repetidamente em novos locais.
Ao ligar a vigilância genômica ao movimento sazonal das aves silvestres, o estudo oferece uma imagem mais precisa de como uma linhagem viral específica pode passar de emergir para alcançar ampla distribuição geográfica em pouco tempo. Ele também mostra o quanto depende da manutenção de sistemas de vigilância capazes de detectar essas mudanças antes que elas se tornem visíveis no gado ou nos números de casos humanos.
O que os pesquisadores relataram
De acordo com o resumo fornecido com o candidato, vírus de influenza aviária altamente patogênica A(H5N1) do clado 2.3.4.4b entraram na América do Norte no fim de 2021 e depois se reassortaram rapidamente com vírus aviários locais. O novo genótipo D1.1 foi detectado em setembro de 2024. Usando dados de vigilância de todo o Canadá e dos EUA, os pesquisadores acompanharam seu surgimento e sua disseminação durante a migração de outono.
O estudo afirma que a análise filodinâmica mostrou que os vírus D1.1 formaram um grupo monofilético. Em termos práticos, isso sustenta a ideia de que os vírus acompanhados na rede de vigilância pertenciam a uma linhagem coerente e recém-expandida, e não a um conjunto disperso de detecções não relacionadas. O artigo também diz que D1.1 deslocou genótipos A(H5) anteriores em várias rotas migratórias, destacando que não se tratou de um evento marginal nas bordas do mapa de vigilância.
O texto fonte também relaciona a expansão de D1.1 a detecções em outros hospedeiros, incluindo 17 casos humanos, quatro dos quais foram graves ou fatais. Ao mesmo tempo, o resumo observa que os marcadores de adaptação a mamíferos encontrados em casos humanos não foram detectados nos vírus de aves silvestres analisados no estudo. Essa distinção é importante: ela sugere que os achados de vigilância em aves silvestres não mostraram diretamente as mesmas assinaturas adaptativas relatadas nos casos humanos.
Por que isso importa além da vigilância de aves
O estudo está na interseção entre ecologia de vida silvestre, saúde animal e saúde humana. Um genótipo em rápida expansão em aves silvestres não é apenas uma questão de conservação ou veterinária; é também um alerta sobre a velocidade com que a ecologia da influenza pode mudar. Quando uma linhagem se estabelece ao longo de rotas migratórias, aumentam as oportunidades de eventos de spillover, exposição agrícola e transmissão entre espécies.
O resumo não afirma que D1.1 tenha adquirido por si só os marcadores de adaptação a mamíferos vistos em infecções humanas, e essa cautela faz parte do ponto. O risco de influenza é moldado por uma combinação em movimento de genética viral, exposição do hospedeiro e oportunidade ecológica. Um genótipo pode se tornar epidemiologicamente importante mesmo sem exibir imediatamente todas as mutações associadas à adaptação em pessoas.
Isso torna a vigilância genômica precoce e ampla especialmente valiosa. O uso de vigilância ativa e passiva pelo artigo indica que nenhum método isolado de coleta basta para um vírus que pode circular em escala continental. Detectar um novo genótipo é um passo. Entender se ele está substituindo outros, quão amplamente está se movendo e se aparece em outros hospedeiros são perguntas diferentes que exigem amostragem contínua.
O que o artigo diz e o que não diz
O material-fonte sustenta várias conclusões claras. D1.1 surgiu como um reassortante detectado em setembro de 2024. Ele se espalhou rapidamente em aves silvestres durante a migração de outono de 2024. Formou um grupo monofilético na análise dos autores e deslocou genótipos A(H5) anteriores em várias rotas migratórias. O resumo acrescenta que vírus candidatos a vacina mantiveram reatividade cruzada antigênica com as cepas D1.1.
Esse último ponto é relevante porque sugere que, com base nos achados relatados pelos autores, os candidatos vacinais não se tornaram antigênicamente irrelevantes com a ascensão desse genótipo. Isso não encerra a discussão de risco, mas indica que a mudança viral e a preparação vacinal não divergiram imediatamente da forma que mais preocupa autoridades de saúde pública.
O resumo não traz um detalhamento geográfico completo, uma cronologia mês a mês do deslocamento nem os detalhes completos do contexto dos casos humanos. Esses detalhes podem estar no artigo completo, mas não constam no texto-fonte fornecido. O que pode ser dito com confiança é que o estudo documenta uma reconfiguração rápida e significativa do cenário do H5N1 em aves silvestres da América do Norte ao longo de uma única temporada migratória.
Um sinal para a era da vigilância
A lição mais ampla é que a vigilância da influenza está cada vez mais parecida com uma corrida contra a recombinação e o movimento viral. Quando uma linhagem é amplamente discutida em público, ela talvez já tenha atravessado várias rotas migratórias e alcançado múltiplos contextos de hospedeiro. O relatório sobre D1.1 mostra por que o acompanhamento genômico se tornou infraestrutura essencial, e não apenas uma ferramenta de pesquisa de nicho.
Para formuladores de políticas e agências de saúde, o estudo reforça uma mensagem familiar, mas ainda urgente: ameaças emergentes de influenza costumam aparecer primeiro em sistemas ecológicos, não em hospitais. Para pesquisadores, ele oferece um estudo de caso de quão rápido uma linhagem reassortante pode se estabelecer. E para o público em geral, é um lembrete de que as histórias de influenza aviária já não são incidentes isolados de fazendas ou da vida silvestre. São eventos de sistemas continentais que exigem atenção contínua muito antes de qualquer contagem de casos humanos chegar às manchetes.
Este artigo é baseado em reportagem da Nature Medicine. Leia o artigo original.
Originally published on nature.com