Un nuevo genotipo de H5N1 avanzó con rapidez por las rutas migratorias
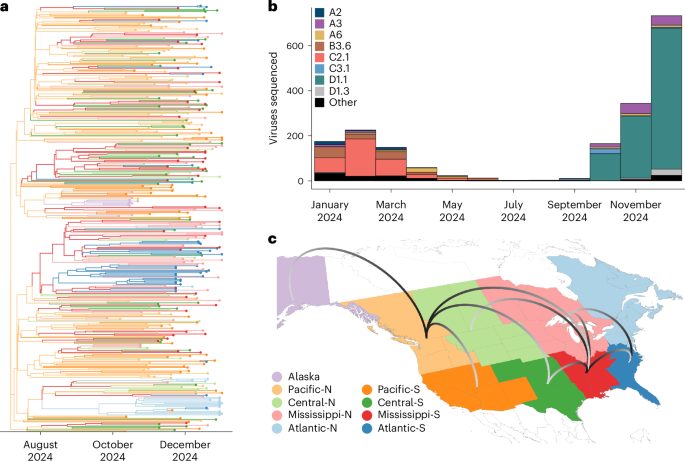
Un estudio publicado en línea en Nature Medicine el 15 de abril de 2026 informa que un genotipo de influenza aviar altamente patógena recientemente clasificado, D1.1, se expandió con rapidez en aves silvestres de Norteamérica durante la temporada migratoria de 2024. El artículo describe al virus como un reasortante detectado por primera vez en septiembre de 2024 y seguido después mediante programas de vigilancia activa y pasiva en Canadá y Estados Unidos.
La conclusión central no es solo que el H5N1 siguiera presente en poblaciones de aves silvestres, sino que un genotipo distinto parece haberse propagado con suficiente rapidez como para desplazar a linajes A(H5) anteriores en varias rutas migratorias. Eso importa porque las rutas migratorias son los canales por los que la influenza aviar puede desplazarse a largas distancias, cruzar jurisdicciones y volver a sembrar brotes repetidamente en nuevos lugares.
Al vincular la vigilancia genómica con el movimiento estacional de las aves silvestres, el estudio ofrece una imagen más nítida de cómo un linaje viral específico puede pasar de emerger a alcanzar un amplio alcance geográfico en poco tiempo. También muestra cuánto depende de mantener sistemas de vigilancia capaces de detectar esos cambios antes de que se hagan visibles en el ganado o en los conteos de casos humanos.
Lo que informaron los investigadores
Según el resumen proporcionado con el candidato, los virus de influenza aviar altamente patógena A(H5N1) del clado 2.3.4.4b entraron en Norteamérica a finales de 2021 y luego se reasortaron con rapidez con virus de influenza aviar locales. El nuevo genotipo D1.1 se detectó en septiembre de 2024. Usando datos de vigilancia de Canadá y Estados Unidos, los investigadores siguieron su aparición y propagación durante la migración de otoño.
El estudio dice que el análisis filodinámico mostró que los virus D1.1 formaban un grupo monofilético. En términos prácticos, eso respalda la idea de que los virus seguidos en la red de vigilancia pertenecían a un linaje coherente y recién expandido, en lugar de ser una colección dispersa de detecciones no relacionadas. El artículo añade además que D1.1 desplazó a genotipos A(H5) anteriores en varias rutas migratorias, lo que subraya que no se trató de un evento marginal en los bordes del mapa de vigilancia.
El texto fuente también vincula la expansión de D1.1 con detecciones en otros hospedadores, incluidos 17 casos humanos, cuatro de ellos graves o fatales. Al mismo tiempo, el resumen señala que los marcadores de adaptación a mamíferos hallados en casos humanos no se detectaron en los virus de aves silvestres analizados en el estudio. Esa distinción es importante: sugiere que los hallazgos de vigilancia en aves silvestres no mostraron directamente las mismas señales adaptativas reportadas en los casos humanos.
Por qué esto importa más allá de la vigilancia de aves
El estudio se sitúa en la intersección entre ecología de vida silvestre, salud animal y salud humana. Un genotipo de expansión rápida en aves silvestres no es solo un asunto de conservación o veterinario; también es una advertencia sobre la velocidad con la que puede cambiar la ecología de la influenza. Cuando un linaje se establece a lo largo de rutas migratorias, aumentan las oportunidades de eventos de salto, exposición agrícola y transmisión entre especies.
El resumen no afirma que D1.1 haya adquirido por sí mismo los marcadores de adaptación a mamíferos vistos en las infecciones humanas, y esa cautela es parte del punto. El riesgo de influenza está moldeado por una combinación en movimiento de genética viral, exposición del hospedador y oportunidad ecológica. Un genotipo puede volverse epidemiológicamente importante incluso sin mostrar de inmediato todas las mutaciones asociadas con adaptación en personas.
Eso hace que la vigilancia genómica temprana y amplia sea especialmente valiosa. El uso de vigilancia activa y pasiva por parte del artículo indica que ningún método de recolección por sí solo basta para un virus que puede circular a escala continental. Detectar un nuevo genotipo es un paso. Entender si está reemplazando a otros, qué tan ampliamente se está moviendo y si aparece en otros hospedadores son preguntas distintas que requieren muestreo sostenido.
Lo que dice y no dice el artículo
El material fuente respalda varias conclusiones claras. D1.1 surgió como un reasortante recién detectado en septiembre de 2024. Se propagó rápidamente en aves silvestres durante la migración otoñal de 2024. Formó un grupo monofilético en el análisis de los autores y desplazó a genotipos A(H5) anteriores en varias rutas migratorias. El resumen añade que los virus candidatos para vacuna conservaron reactividad cruzada antigénica con las cepas D1.1.
Ese último punto es notable porque sugiere que, según los hallazgos reportados por los autores, los candidatos vacunales no quedaron antigénicamente irrelevantes por el ascenso de este genotipo. No elimina el riesgo, pero sí indica que el cambio viral y la preparación de vacunas no divergieron de inmediato de la forma que más temen las autoridades de salud pública.
El resumen no ofrece un desglose geográfico completo, una cronología mes a mes del desplazamiento ni los detalles completos del contexto de los casos humanos. Esos datos pueden estar en el artículo completo, pero no están contenidos en el texto fuente proporcionado. Lo que sí puede decirse con confianza es que el estudio documenta una reconfiguración rápida y significativa del panorama de H5N1 en aves silvestres de Norteamérica durante una sola temporada migratoria.
Una señal para la era de la vigilancia
La lección más amplia es que la vigilancia de influenza es cada vez más una carrera contra la recombinación y el movimiento viral. Para cuando un linaje se discute ampliamente en público, quizá ya haya atravesado varias rutas migratorias y pasado a varios entornos hospedadores. El informe sobre D1.1 muestra por qué el seguimiento genómico se ha convertido en infraestructura esencial, no en una herramienta de investigación de nicho.
Para los responsables de políticas y las agencias de salud, el estudio refuerza un mensaje familiar pero aún urgente: las amenazas emergentes de influenza suelen hacerse visibles primero en sistemas ecológicos, no en hospitales. Para los investigadores, ofrece un caso de estudio sobre cuán rápido puede establecerse un linaje reasortante. Y para el público en general, recuerda que las historias de influenza aviar ya no son incidentes aislados de granjas o fauna silvestre. Son eventos de sistemas continentales que exigen atención sostenida mucho antes de que aparezca cualquier conteo de casos humanos en los titulares.
Este artículo se basa en un reporte de Nature Medicine. Leer el artículo original.
Originally published on nature.com