Ein neuer H5N1-Genotyp breitete sich rasch entlang der Zugrouten aus
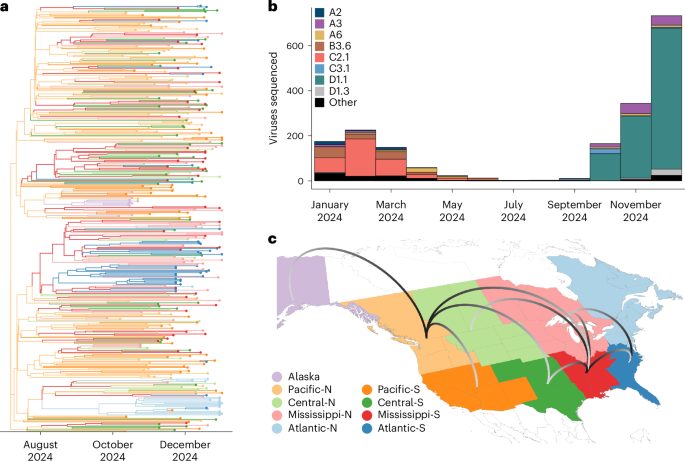
Eine am 15. April 2026 online in Nature Medicine veröffentlichte Studie berichtet, dass sich ein neu klassifizierter hochpathogener aviärer Influenza-Genotyp, D1.1, während der Migrationssaison 2024 schnell in Wildvögeln in Nordamerika ausbreitete. Die Arbeit beschreibt das Virus als Reassortanten, der erstmals im September 2024 entdeckt und anschließend über aktive und passive Überwachungsprogramme in Kanada und den USA verfolgt wurde.
Die zentrale Erkenntnis ist nicht nur, dass H5N1 in Wildvogelpopulationen weiterhin vorhanden war, sondern dass sich offenbar ein klarer Genotyp so schnell ausbreitete, dass er frühere A(H5)-Linien in mehreren Zugrouten verdrängte. Das ist bedeutsam, weil Zugrouten die Kanäle sind, über die aviäre Influenza große Distanzen zurücklegen, Jurisdiktionen überqueren und Ausbrüche an neuen Orten immer wieder neu anstoßen kann.
Indem die Studie genomische Überwachung mit der saisonalen Bewegung von Wildvögeln verknüpft, zeichnet sie ein schärferes Bild davon, wie eine bestimmte Viruslinie in kurzer Zeit von ihrem Auftauchen zu einer breiten geografischen Ausbreitung gelangen kann. Sie zeigt auch, wie sehr es darauf ankommt, Überwachungssysteme aufrechtzuerhalten, die solche Verschiebungen erkennen können, bevor sie in der Tierhaltung oder in Fallzahlen beim Menschen sichtbar werden.
Was die Forschenden berichtet haben
Laut der mit dem Kandidaten gelieferten Zusammenfassung gelangten hochpathogene aviäre Influenza-A(H5N1)-Viren der Klade 2.3.4.4b Ende 2021 nach Nordamerika und reassortierten dann rasch mit lokalen aviären Influenza-Viren. Der neu beobachtete D1.1-Genotyp wurde im September 2024 nachgewiesen. Mithilfe von Überwachungsdaten aus Kanada und den USA verfolgten die Forschenden sein Auftauchen und seine Ausbreitung während der Herbstmigration.
Die Studie sagt, dass die phyldynamische Analyse zeigte, dass die D1.1-Viren eine monophyletische Gruppe bildeten. Praktisch stützt das die Annahme, dass die in dem Überwachungsnetzwerk verfolgten Viren zu einer kohärenten, neu expandierten Linie gehörten und nicht zu einer lose zusammengewürfelten Reihe nicht zusammenhängender Nachweise. Die Arbeit sagt außerdem, dass D1.1 frühere A(H5)-Genotypen in mehreren Zugrouten verdrängte, was unterstreicht, dass es sich nicht um ein Randereignis am äußersten Rand der Überwachungskarte handelte.
Der Quelltext verknüpft die Ausbreitung von D1.1 zudem mit Nachweisen in anderen Wirten, darunter 17 menschliche Fälle, von denen vier schwer oder tödlich waren. Zugleich stellt die Zusammenfassung fest, dass die in menschlichen Fällen gefundenen Marker für Anpassung an Säugetiere in den in der Studie untersuchten Wildvogelviren nicht nachgewiesen wurden. Diese Unterscheidung ist wichtig: Sie legt nahe, dass die Überwachungsergebnisse bei Wildvögeln nicht direkt dieselben Anpassungssignale zeigten, die in den menschlichen Fällen berichtet wurden.
Warum das über die Vogelüberwachung hinaus wichtig ist
Die Studie liegt an der Schnittstelle von Wildökologie, Tiergesundheit und menschlicher Gesundheit. Ein rasch expandierender Genotyp in Wildvögeln ist nicht nur ein Naturschutz- oder Veterinärthema; er ist auch eine Warnung vor der Geschwindigkeit, mit der sich die Influenza-Ökologie verändern kann. Wenn sich eine Linie entlang von Zugrouten etabliert, steigen die Chancen für Spillover-Ereignisse, landwirtschaftliche Exposition und Übertragung zwischen Arten.
Die Zusammenfassung behauptet nicht, dass D1.1 selbst die bei menschlichen Infektionen beobachteten Säugetier-Anpassungsmarker erworben hat, und genau diese Vorsicht ist Teil der Aussage. Das Influenza-Risiko wird durch eine sich bewegende Kombination aus Virusgenetik, Wirtsexposition und ökologischer Gelegenheit geprägt. Ein Genotyp kann epidemiologisch relevant werden, ohne sofort alle Mutationen zu zeigen, die mit einer Anpassung an den Menschen verbunden sind.
Das macht frühe, breit angelegte genomische Überwachung besonders wertvoll. Die in der Arbeit erwähnte aktive und passive Überwachung zeigt, dass keine einzelne Erhebungsmethode für ein Virus genügt, das kontinentweit zirkulieren kann. Einen neuen Genotyp zu entdecken, ist nur ein Schritt. Zu verstehen, ob er andere verdrängt, wie weit er sich bewegt und ob er in weiteren Wirten auftaucht, sind separate Fragen, die eine fortlaufende Probenahme erfordern.
Was die Arbeit sagt und was nicht
Das Quellenmaterial stützt mehrere klare Schlussfolgerungen. D1.1 trat als neu entdeckter Reassortant im September 2024 auf. Er verbreitete sich während der Herbstmigration 2024 rasch in Wildvögeln. In der Analyse der Autorinnen und Autoren bildete er eine monophyletische Gruppe und verdrängte frühere A(H5)-Genotypen in mehreren Zugrouten. Die Zusammenfassung ergänzt, dass Impfstoffkandidaten eine antigene Kreuzreaktivität mit D1.1-Stämmen beibehielten.
Dieser letzte Punkt ist bemerkenswert, weil er nahelegt, dass die Impfstoffkandidaten nach den von den Autoren berichteten Ergebnissen durch den Aufstieg dieses Genotyps nicht antigen irrelevant wurden. Das beendet die Risikodebatte nicht, zeigt aber, dass sich Viruswandel und Impfvorbereitung nicht sofort so auseinanderentwickelten, wie es die öffentliche Gesundheit am meisten fürchtet.
Die Zusammenfassung liefert keine vollständige geografische Aufschlüsselung, keine Monat-für-Monat-Chronologie der Verdrängung und keine kompletten Details zum Kontext der menschlichen Fälle. Diese Details könnten in der Vollversion stehen, sind aber im bereitgestellten Text nicht enthalten. Sicher sagen lässt sich, dass die Studie eine schnelle und folgenreiche Umgestaltung der H5N1-Landschaft bei nordamerikanischen Wildvögeln während einer einzigen Migrationssaison dokumentiert.
Ein Signal für das Überwachungszeitalter
Die breitere Lehre ist, dass die Influenza-Überwachung zunehmend zu einem Wettlauf gegen Reassortierung und Virusbewegung wird. Wenn eine Linie in der Öffentlichkeit breit diskutiert wird, hat sie möglicherweise bereits mehrere Zugrouten durchquert und verschiedene Wirtskontexte erreicht. Der D1.1-Bericht zeigt, warum genomisches Tracking zu einer essenziellen Infrastruktur geworden ist und nicht bloß zu einem Nischenforschungstool.
Für politische Entscheidungsträger und Gesundheitsbehörden bekräftigt die Studie eine vertraute, aber weiterhin dringliche Botschaft: Neue Influenza-Bedrohungen werden oft zuerst in ökologischen Systemen sichtbar, nicht in Krankenhäusern. Für Forschende liefert sie eine Fallstudie dazu, wie schnell sich eine reassortierte Linie etablieren kann. Und für die breite Öffentlichkeit erinnert sie daran, dass Vogelgrippe-Geschichten nicht mehr nur isolierte Ereignisse auf Farmen oder in der Wildnis sind. Es handelt sich um kontinentale Systemereignisse, die anhaltende Aufmerksamkeit erfordern, lange bevor in den Schlagzeilen irgendeine Zahl menschlicher Fälle erscheint.
Dieser Artikel basiert auf einem Bericht von Nature Medicine. Zum Originalartikel.
Originally published on nature.com